文章目录
- 聚类
- Kmeans
- 时间复杂度
- sklearn.cluster.KMeans
- n_clusters
- 模型评估指标
- 轮廓系数
- 卡林斯基-哈拉巴斯指数
- init & random_state & n_init:初始质心
- max_iter & tol
- k_means函数
聚类
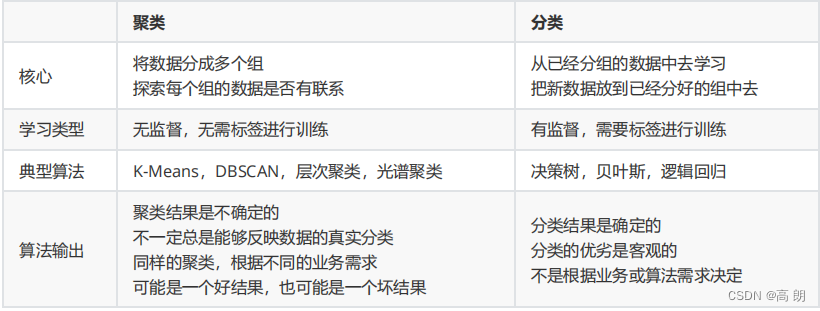
聚类就是按照某个特定标准(如距离准则)把一个数据集分割成不同的类或簇,使得同一个簇内的数据对象的相似性尽可能大,同时不在同一个簇中的数据对象的差异性也尽可能地大。即聚类后同一类的数据尽可能聚集到一起,不同类的数据尽量远离。
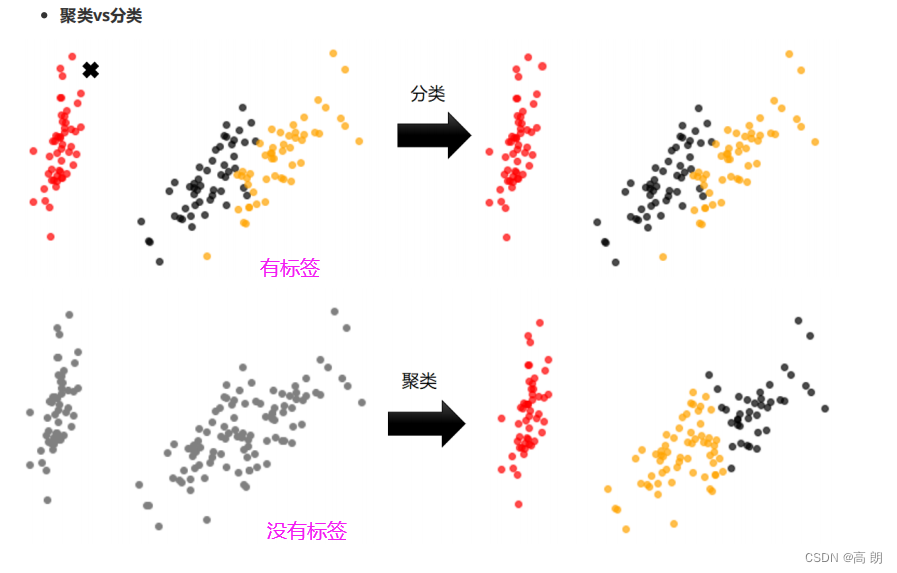
和分类相似,每个实例都分配给一个组,但不同的是:聚类 (Clustering)简单地说就是把相似的东西分到一组,聚类的时候,我们并不关心某一类是什么,我们需要实现的目标只是把相似的东西聚到一起。
聚类 (Clustering)通常并不需要使用训练数据进行学习,这在机器学习中被称作无监督学习 (unsupervised learning),通常只需要知道如何计算相似度就可以开始工作了。
不同的聚类算法有不同的应用背景,有的适合于大数据集,可以发现任意形状的聚簇;有的算法思想简单,适用于小数据集。
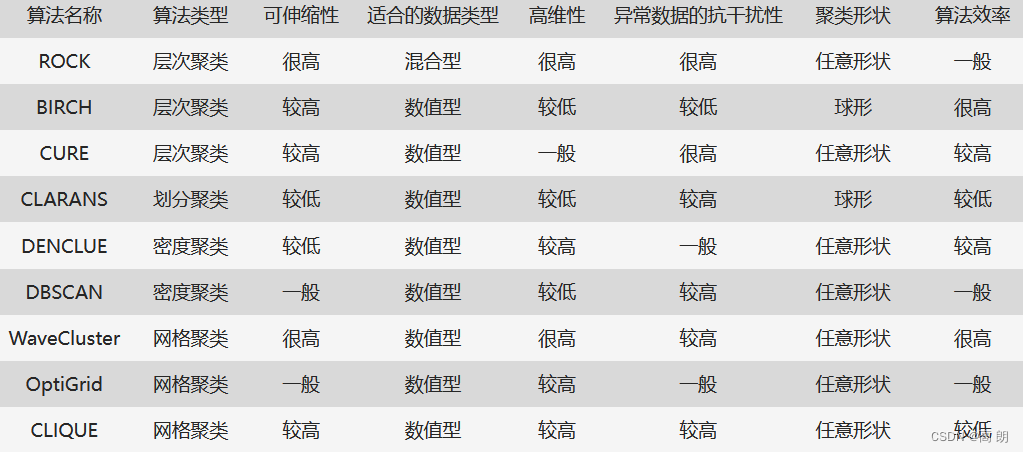
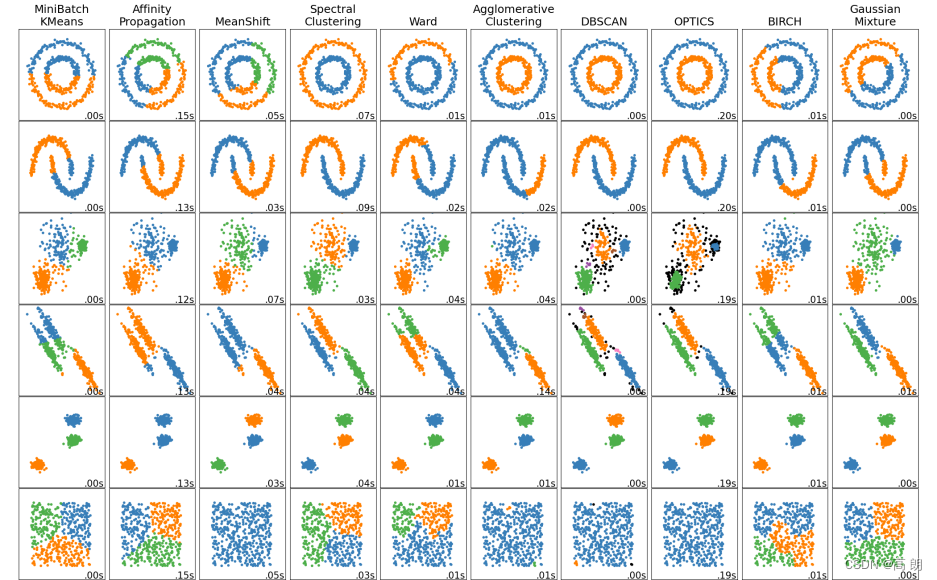
接下来通过将通过sklearn集成的Kmeans算法来理解Kmeans聚类算法,附sklearn上聚类算法的类和接口:
聚类算法在sklearn中有两种表现形式,一种是类,需要实例化,训练并使用接口和属性来调用结果。另一种是函数(function),只需要输入特征矩阵和超参数,即可返回聚类的结果和各种指标。

Kmeans
基于划分的方法是简单、常用的一种聚类方法,它通过将对象划分为互斥的簇进行聚类, 每个对象属于且仅属于一个簇;划分结果旨在使簇之间的相似性低,簇内部的相似度高。
K-Means算法是一种基于划分的简单算法,与其他聚类算法相比,能够非常快速、高效地对此类数据集进行聚类,通常只需几次迭代即可。
K-Means极易实现而且计算效率也很高。
核心:簇和质心
KMeans算法将一组N个样本的特征矩阵X划分为K个无交集的簇,直观上来看是簇是一组一组聚集在一起的数据,在一个簇中的数据就认为是同一类。簇就是聚类的结果表现。
簇中所有数据的均值 μ j μ_j μj通常被称为这个簇的“质心”(centroids)。在一个二维平面中,一簇数据点的质心的横坐标就是这一簇数据点的横坐标的均值,质心的纵坐标就是这一簇数据点的纵坐标的均值。同理可推广至高维空间。
通过计算样本点与质心的距离,与质心相近的样本点划分为同一类簇。
在KMeans算法中,簇的个数K是一个超参数,需要我们人为输入来确定。KMeans的核心任务就是根据我们设定好的K,找出K个最优的质心,并将离这些质心最近的数据分别分配到这些质心代表的簇中去。
具体过程:
迭代停止,质心的位置会不再变化:当我们找到一个质心,在每次迭代中被分配到这个质心上的样本都是一致的,即每次新生成的簇都是一致的,所有的样本点都不会再从一个簇转移到另一个簇,质心就不会变化了。
这个过程在可以由下图来显示,我们规定,将数据分为4簇(K=4),其中白色X代表质心的位置:

在数据集下多次迭代(iteration),就会有:
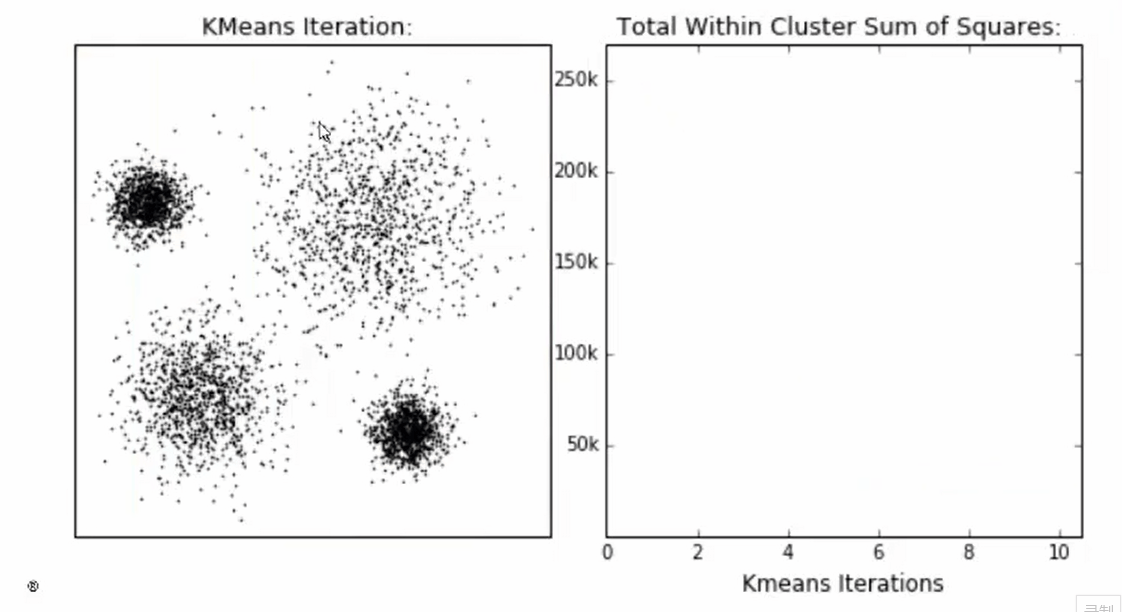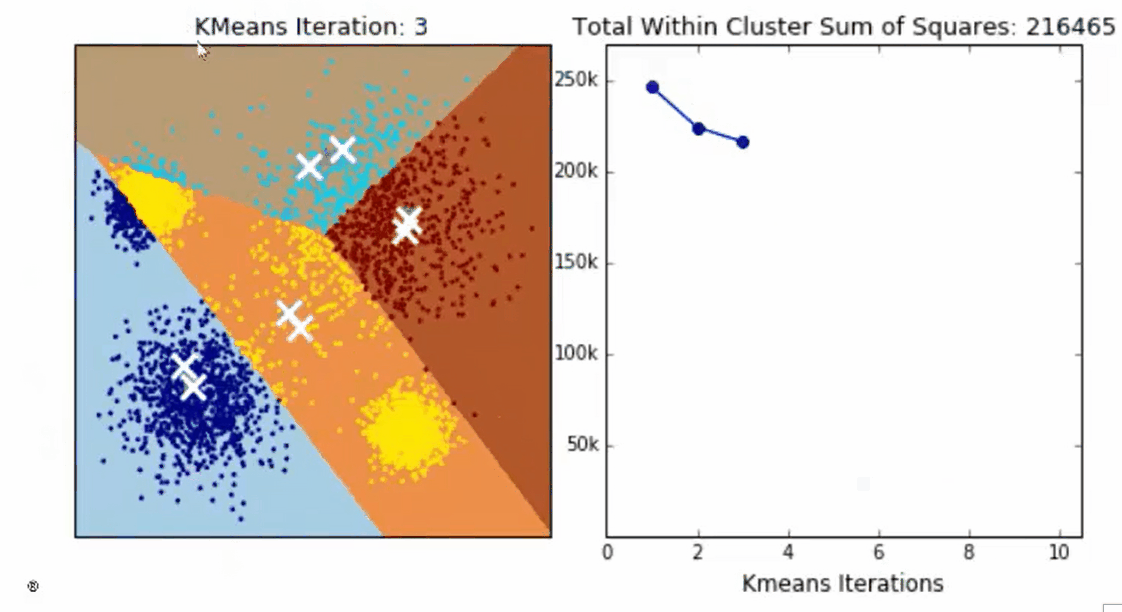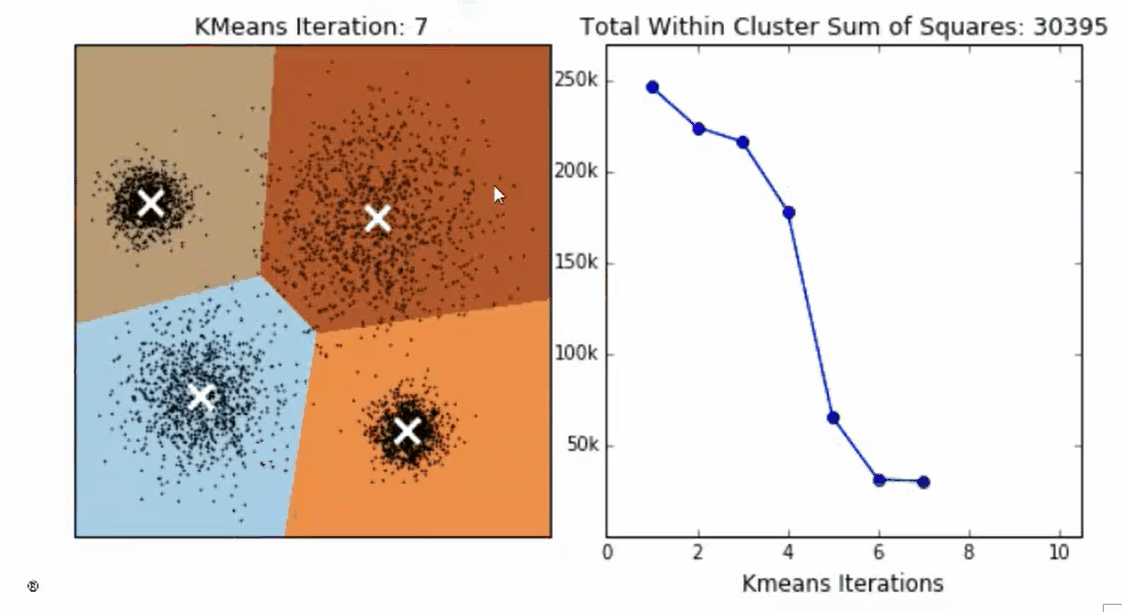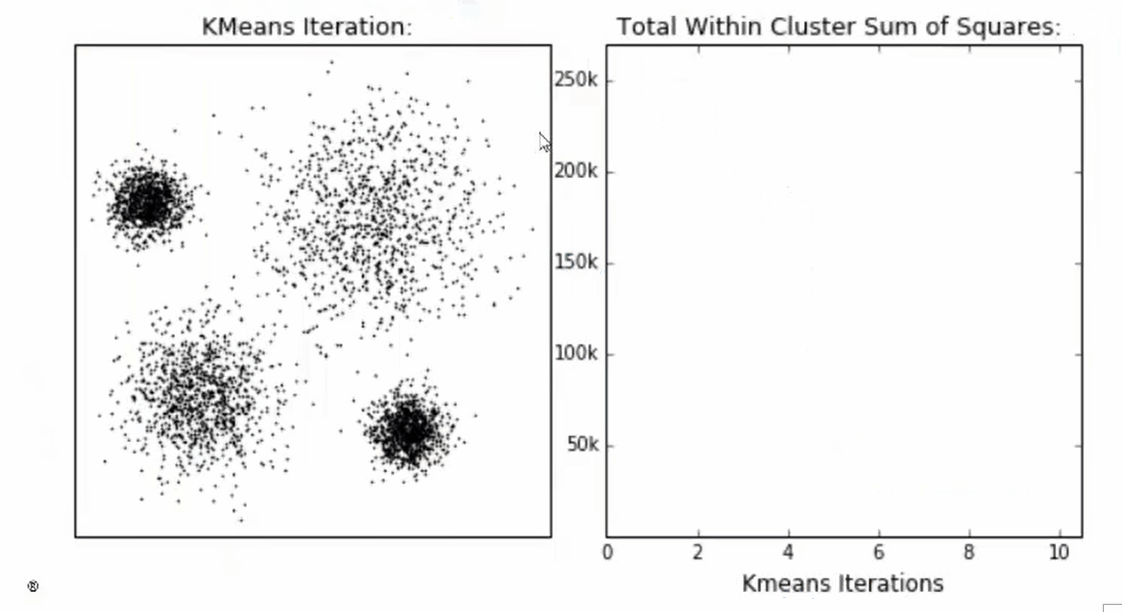 第六次迭代之后,基本上质心的位置就不再改变了,生成的簇也变得稳定。此时我们的聚类就完成了,我们可以明显看出,KMeans按照数据的分布,将数据聚集成了我们规定的4类,接下来我们就可以按照我们的业务需求或者算法需求,对这四类数据进行不同的处理。
第六次迭代之后,基本上质心的位置就不再改变了,生成的簇也变得稳定。此时我们的聚类就完成了,我们可以明显看出,KMeans按照数据的分布,将数据聚集成了我们规定的4类,接下来我们就可以按照我们的业务需求或者算法需求,对这四类数据进行不同的处理。
相似度是通过样本间的距离来衡量它们的,两个样本距离越远,则相似度越低,否则相似度越高。追求“簇内差异小,簇外差异大”,差异是由样本点到其所在簇的质心的距离来衡量。
对于一个簇来说,所有样本点到质心的距离之和越小,我们就认为这个簇中的样本越相似,簇内差异就越小。
计算样本点到质心距离的方式:
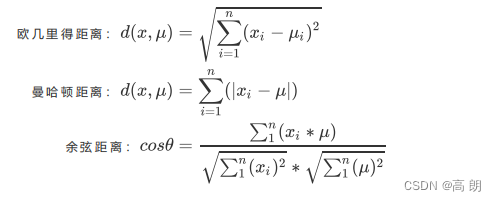
x
x
x表示簇中的一个样本点,
μ
μ
μ表示该簇中的质心,n表示每个样本点中的特征数目,i表示组成点
x
x
x 的每个特征。【数字与数字之间的距离主要采用欧几里得,余弦距离适用于文本与文本之间的距离】
- 簇内平方和(cluster Sum of Square),又叫做
Inertia:簇内所有样本点到该簇质心的距离之和。 - 整体平方和(Total Cluster Sum ofSquare),又叫做
total inertia:所有簇的簇内平方和相加。
以欧几里得距离为例:(k个簇,每个簇m个样本,每个样本n个特征)

Total Inertia越小,代表着每个簇内样本越相似,聚类的效果就越好。因此KMeans追求的是,求解能够让Inertia最小化的质心。实际上,在质心不断变化不断迭代的过程中,总体平方和是越来越小的。当整体平方和最小的时候,质心就不再发生变化了。
是属于最优化的问题:我们在一个固定的簇数K下,最小化总体平方和来求解最佳质心,并基于质心的存在去进行聚类。
时间复杂度
该算法的计算复杂度在实例数m,簇数k和维度n方面通常是线性的,但是,仅当数据具有聚类结构时才如此。如果不是这样,那么在最坏的情况下,复杂度会随着实例数量的增加而呈指数增加。实际上,这种情况很少发生,并且K-Means通常是最快的聚类算法之一。
sklearn.cluster.KMeans
class sklearn.cluster.KMeans (
n_clusters=8,
init=’k-means++’,
n_init=10,
max_iter=300,
tol=0.0001,
precompute_distances=’auto’,
verbose=0,
random_state=None,
copy_x=True,
n_jobs=None,
algorithm=’auto’)
- 参数:


- 属性:

- 接口:
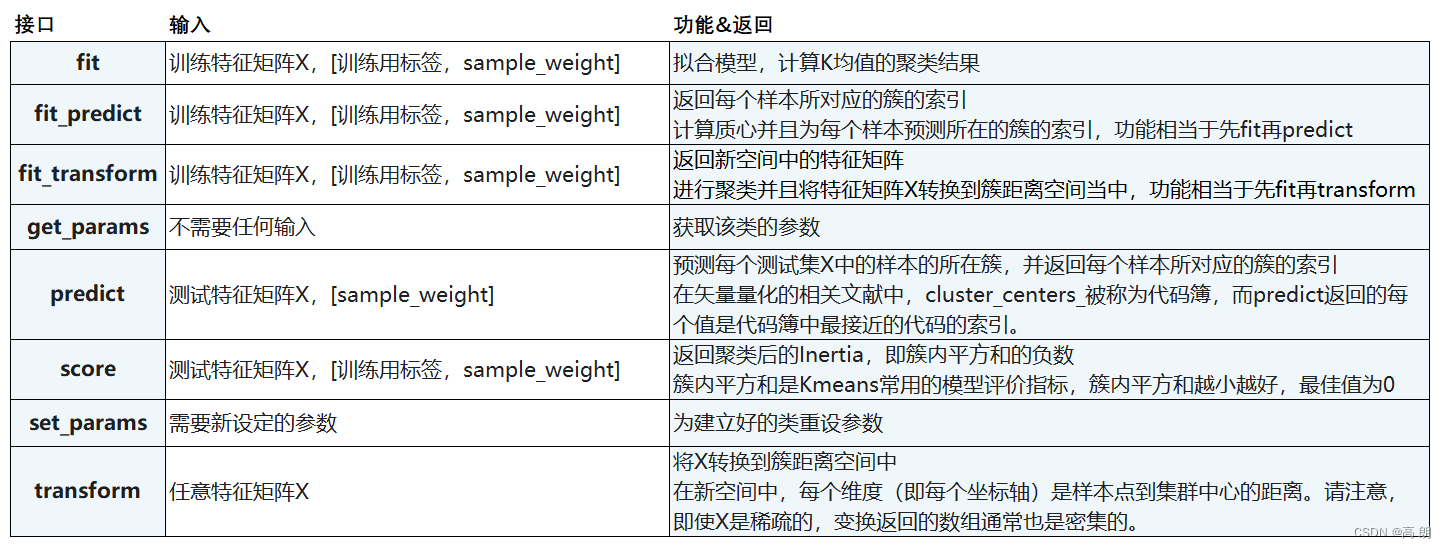
一些重要的参数代码示例理解:
n_clusters
n_clusters是KMeans中的k,表示着我们告诉模型我们要分几类。这是KMeans当中唯一一个必填的参数,默认为8类,但通常我们的聚类结果会是一个小于8的结果。通常,在开始聚类之前,我们并不知道n_clusters究竟是多少,因此我们要对它进行探索。
from sklearn.datasets import make_blobs # 创建簇类数据
import matplotlib.pyplot as plt
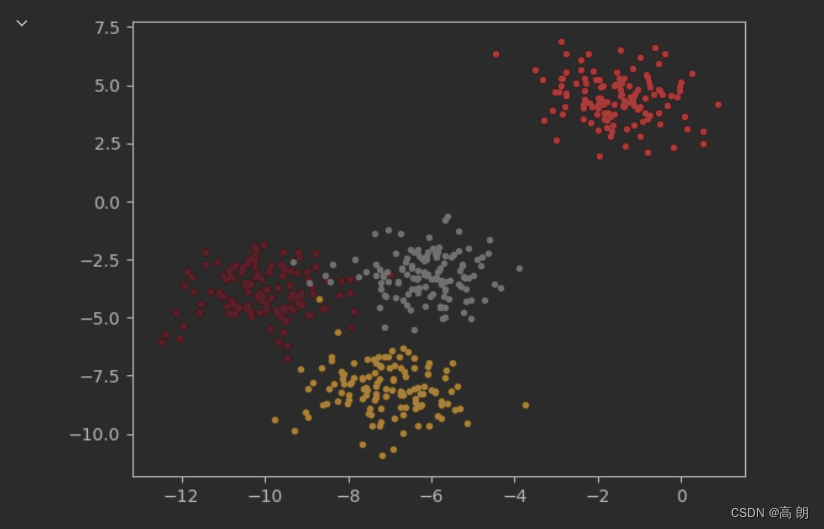
X, y = make_blobs(n_samples=500,n_features=2,centers=4,random_state=1)
# 500个样本,2个特征,4类的数据集,有标签的,方便与聚簇后的结果进行比较
看一下真实的分类:
color = ["red","pink","orange","gray"]
fig, ax1 = plt.subplots(1) # 参数:生成子图的数量
for i in range(4):
ax1.scatter(X[y==i, 0], X[y==i, 1]
,marker='o' #点的形状
,s=8 #点的大小
,c=color[i]
)
plt.show()
 接下来,通过kmeans来对没有标签的上面的数据进行聚簇,看看和真实的差异:
接下来,通过kmeans来对没有标签的上面的数据进行聚簇,看看和真实的差异:
- 簇为3类时:
from sklearn.cluster import KMeans
n_clusters = 3
cluster = KMeans(n_clusters=n_clusters, random_state=0, n_init=10).fit(X)
y_pred = cluster.labels_ # 查看每个点对应的标签
y_pred # 每个样本对应的标签
 可以一步到位,不需要
可以一步到位,不需要fit后再查看labels_ ,直接fit_predict搞定
pre = cluster.fit_predict(X) # 学习数据X并对X进行预测
(pre != y_pred).sum() # 看看和上面是不是一样
如何数据量太多,太慢了,可以先聚类一部分数据,【有时候少部分数据就可以找到很完美的质心】迭代找到质心,再进行预测其他数据就可以了,这样可以大大减少时间:
cluster_smallsub = KMeans(n_clusters=n_clusters, random_state=0, n_init=10).fit(X[:200])
y_pred_ = cluster_smallsub.predict(X)
(pre != y_pred).sum()
可以看到只有少量数据聚类的结果不一样。
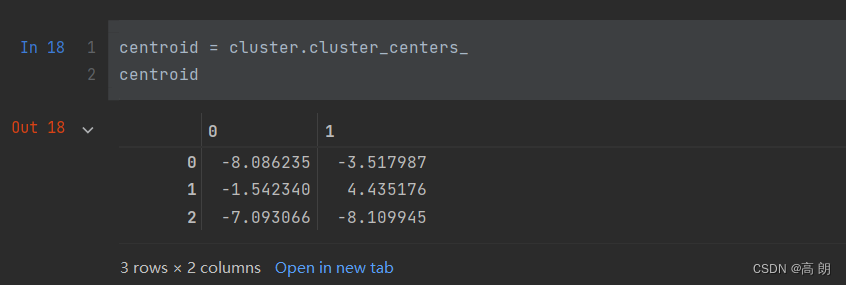
查看质心:cluster_centers_
centroid = cluster.cluster_centers_
centroid
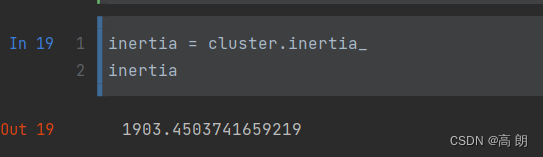
 查看总距离平方和:
查看总距离平方和:inertia_
inertia = cluster.inertia_
inertia
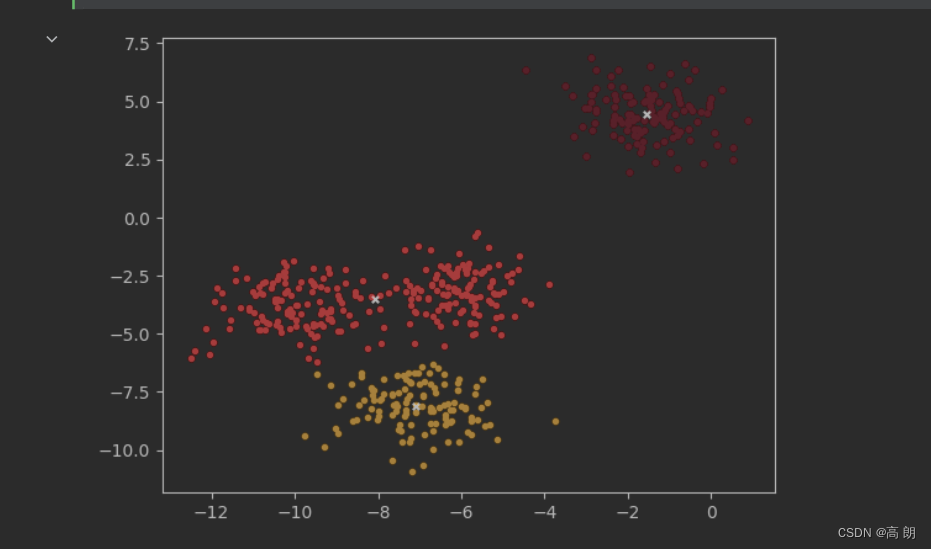
画出簇为3类的分类结果:
color = ["red","pink","orange","gray"]
fig, ax1 = plt.subplots(1)
for i in range(n_clusters):
ax1.scatter(X[y_pred==i, 0], X[y_pred==i, 1]
,marker='o'
,s=8
,c=color[i]
)
ax1.scatter(centroid[:,0],centroid[:,1]
,marker="x"
,s=15
,c="black")
plt.show()
- 簇为4类时:
n_clusters = 4
cluster_ = KMeans(n_clusters=n_clusters, random_state=0, n_init=10).fit(X)
y_pred_4= cluster_.labels_
color = ["red","pink","orange","gray"]
fig, ax1 = plt.subplots(1)
for i in range(4):
ax1.scatter(X[y_pred_4==i, 0], X[y_pred_4==i, 1]
,marker='o' #点的形状
,s=8 #点的大小
,c=color[i]
)
plt.show()
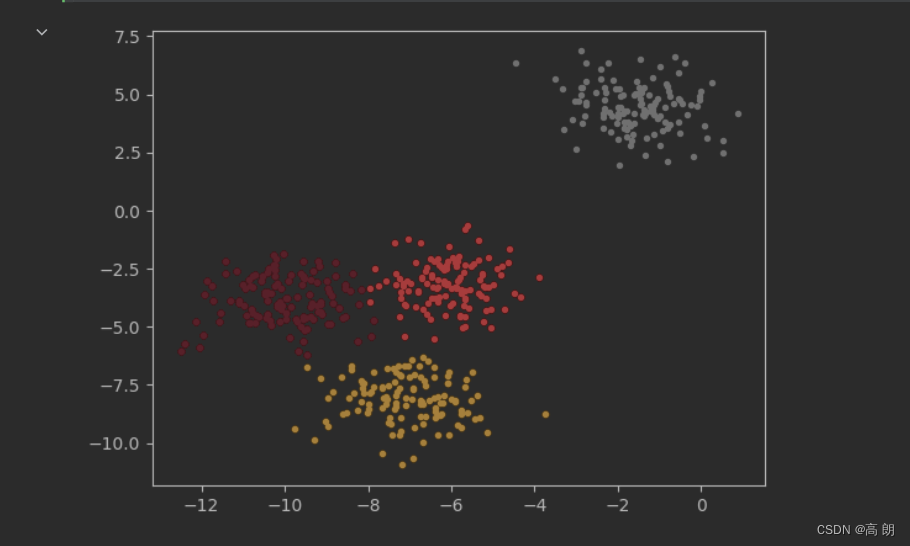 只能说效果真的很好。
只能说效果真的很好。
我们并不知道参数n_clusters取什么值好,也就是分几类,根据前面理论,聚类效果越好,距离平方和Inertia越小。
但是随着n_clusters增大,Inertia是越来越小了。当n_clusters等于样本数时,也就是每个点都质心,那么距离平方和Inertia=0,不能调节k,来降低Inertia的值,然后表示模型的效果变好了
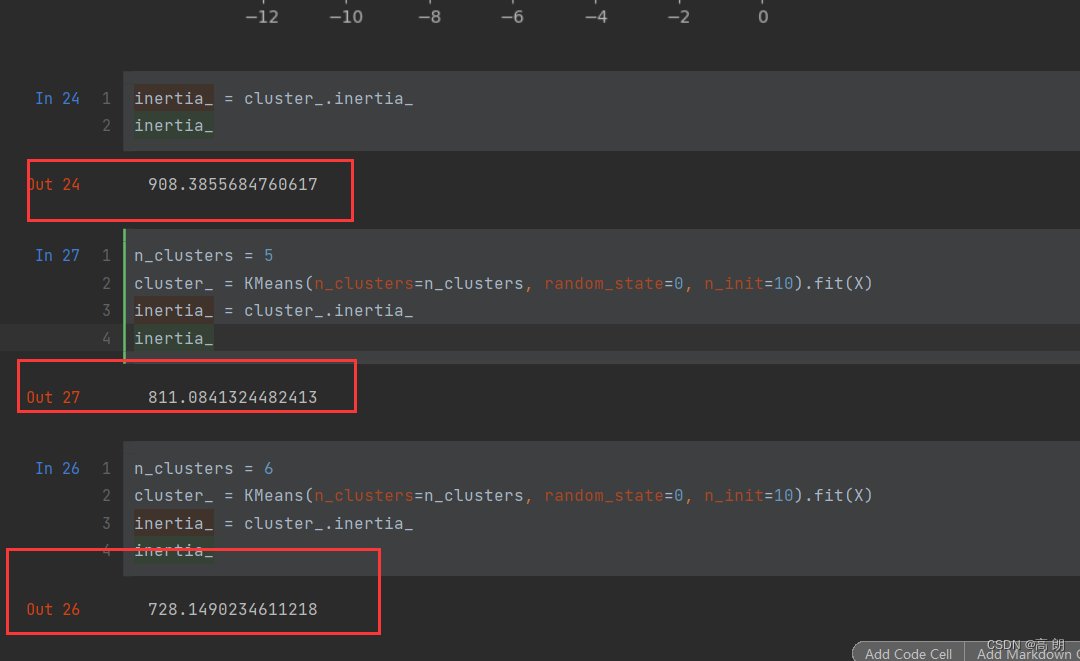
Inertia不是模型评估指标
模型评估指标
聚类模型的结果不是某种标签输出,并且聚类的结果是不确定的,其优劣由业务需求或者算法需求来决定,并且没有永远的正确答案。
轮廓系数
KMeans的目标是确保“簇内差异小,簇外差异大”,根据目标出发,评估聚类的效果是完全依赖于评价簇内的稠密程度(簇内差异小)和簇间的离散程度(簇外差异大)来的。
1)样本与其自身所在的簇中的其他样本的相似度a:等于样本与同一簇中所有其他点之间的平均距离
2)样本与其他簇中的样本的相似度b:等于样本与下一个最近的簇中的所有点之间的平均距离
根据聚类的要求”簇内差异小,簇外差异大“,我们希望b永远大于a,并且大得越多越好。
单个样本的轮廓系数计算为:
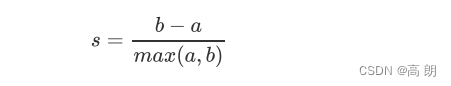
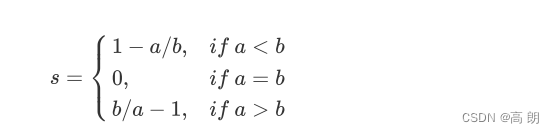
轮廓系数范围是(-1,1),其中值越接近1表示样本与自己所在的簇中的样本很相似,并且与其他簇中的样本不相似,这就是聚簇想要达到的效果。
轮廓系数就为负,表示样本点与簇外的样本更相似,与聚簇的目标背道而驰。
轮廓系数为0,表示两个簇中的样本相似度一致,两个簇本应该是一个簇。
所以轮廓系数越接近于1越好,负数则表示聚类效果非常差。
如果许多样本点具有低轮廓系数甚至负值,说明聚类是不合适的,则需要重新设定聚类的超参数K。
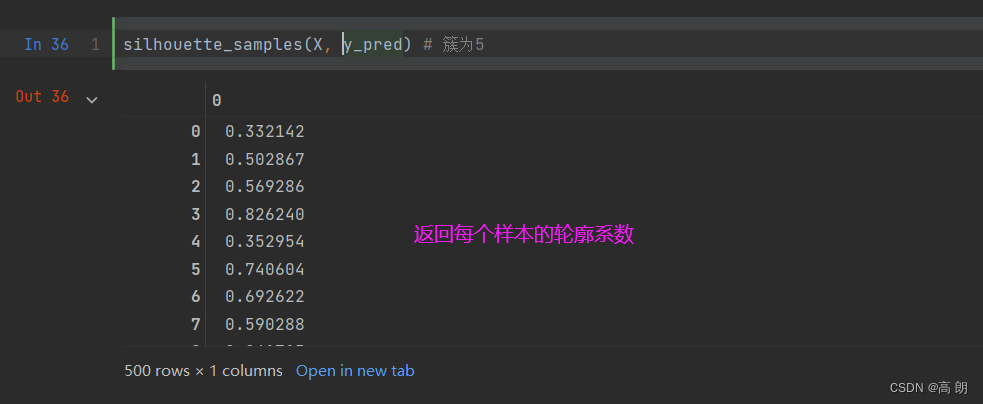
sklearn中,模块metrics中的类silhouette_score是用来计算轮廓系数,它返回的是一个数据集中,返回所有样本的轮廓系数的均值。silhouette_sample,它的参数与轮廓系数一致,但返回的数据集中每个样本自己的轮廓系数。
from sklearn.metrics import silhouette_score
from sklearn.metrics import silhouette_samples
silhouette_score(X,y_pred) # 簇为3
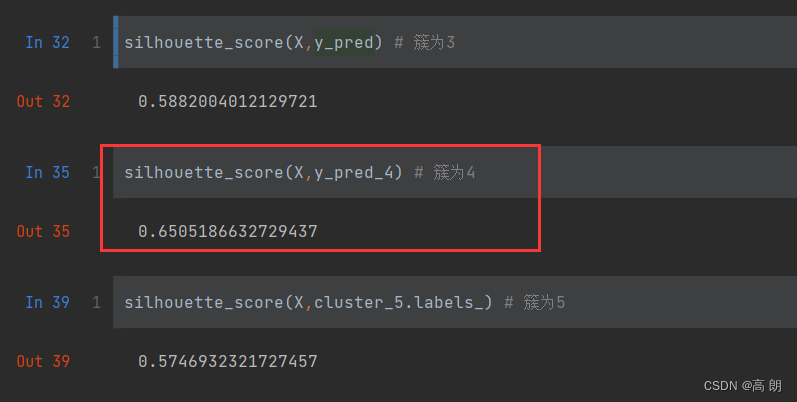 可以看到分4簇时,轮廓系数是最大的,效果最好。
可以看到分4簇时,轮廓系数是最大的,效果最好。
轮廓系数在每个簇的分割比较清洗时表现最好。
轮廓系数在凸型的类上表现会虚高,比如基于密度进行的聚类,或通过DBSCAN获得的聚类结果,如果使用轮廓系数来衡量,则会表现出比真实聚类效果更高的分数。
基于轮廓系数来选择n_clusters:
(每个聚出来的类的轮廓系数是多少,各个类之间的轮廓系数的对比)
from sklearn.cluster import KMeans
from sklearn.metrics import silhouette_samples, silhouette_score
import matplotlib.pyplot as plt
import matplotlib.cm as cm
import numpy as np
for n_clusters in [2,3,4,5,6,7]:
n_clusters = n_clusters
fig, (ax1, ax2) = plt.subplots(1, 2)
fig.set_size_inches(18, 7)
ax1.set_xlim([-0.1, 1])
ax1.set_ylim([0, X.shape[0] + (n_clusters + 1) * 10])
clusterer = KMeans(n_clusters=n_clusters, random_state=10).fit(X)
cluster_labels = clusterer.labels_
silhouette_avg = silhouette_score(X, cluster_labels)
print("For n_clusters =", n_clusters,
"The average silhouette_score is :", silhouette_avg)
sample_silhouette_values = silhouette_samples(X, cluster_labels)
y_lower = 10
for i in range(n_clusters):
ith_cluster_silhouette_values = sample_silhouette_values[cluster_labels == i]
ith_cluster_silhouette_values.sort()
size_cluster_i = ith_cluster_silhouette_values.shape[0]
y_upper = y_lower + size_cluster_i
color = cm.nipy_spectral(float(i)/n_clusters)
ax1.fill_betweenx(np.arange(y_lower, y_upper)
,ith_cluster_silhouette_values
,facecolor=color
,alpha=0.7
)
ax1.text(-0.05
, y_lower + 0.5 * size_cluster_i
, str(i))
y_lower = y_upper + 10
ax1.set_title("The silhouette plot for the various clusters.")
ax1.set_xlabel("The silhouette coefficient values")
ax1.set_ylabel("Cluster label")
ax1.axvline(x=silhouette_avg, color="red", linestyle="--")
ax1.set_yticks([])
ax1.set_xticks([-0.1, 0, 0.2, 0.4, 0.6, 0.8, 1])
colors = cm.nipy_spectral(cluster_labels.astype(float) / n_clusters)
ax2.scatter(X[:, 0], X[:, 1]
,marker='o'
,s=8
,c=colors
)
centers = clusterer.cluster_centers_
# Draw white circles at cluster centers
ax2.scatter(centers[:, 0], centers[:, 1], marker='x',
c="red", alpha=1, s=200)
ax2.set_title("The visualization of the clustered data.")
ax2.set_xlabel("Feature space for the 1st feature")
ax2.set_ylabel("Feature space for the 2nd feature")
plt.suptitle(("Silhouette analysis for KMeans clustering on sample data "
"with n_clusters = %d" % n_clusters),
fontsize=14, fontweight='bold')
plt.show()
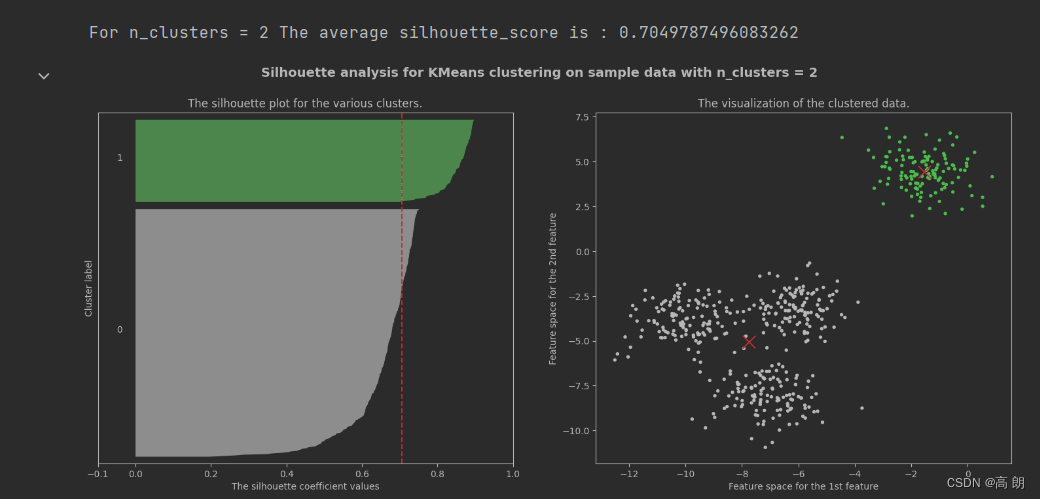
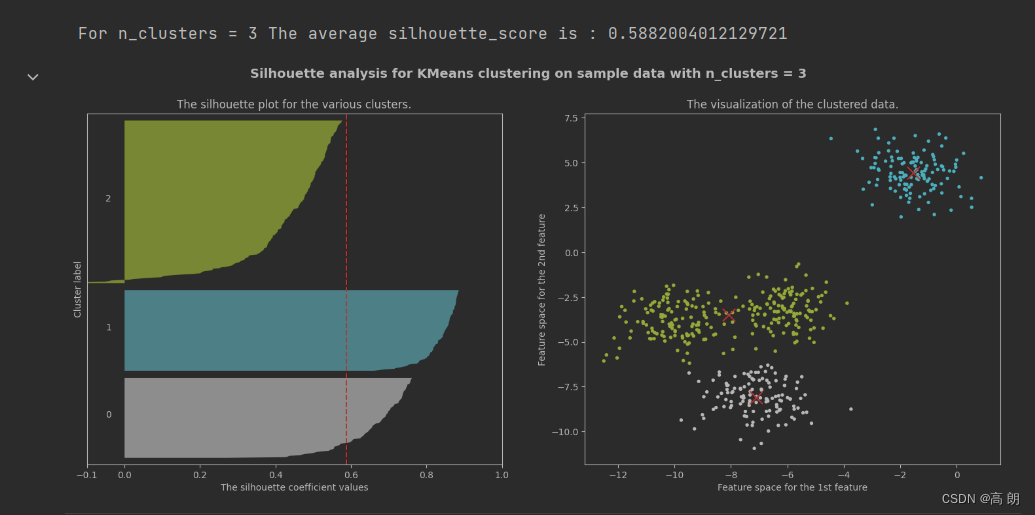

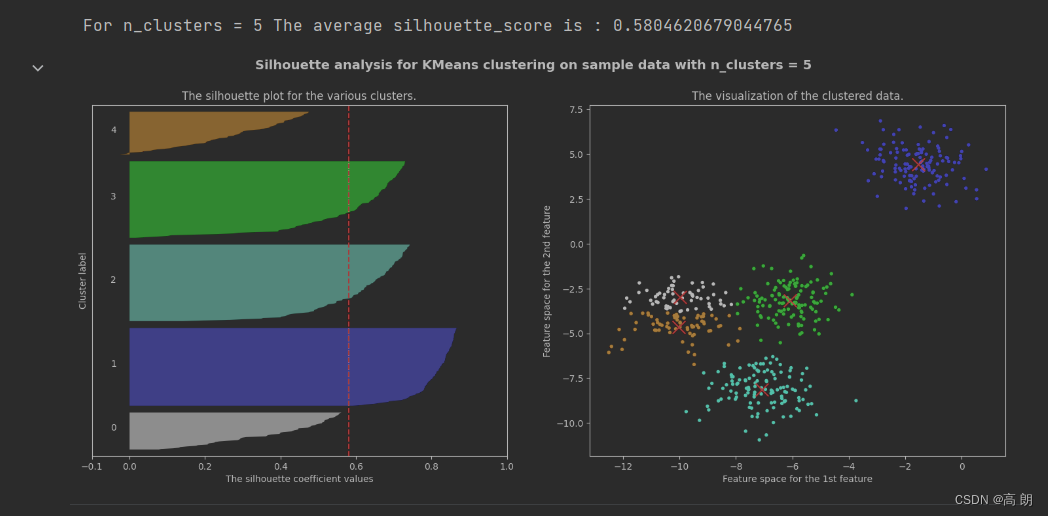
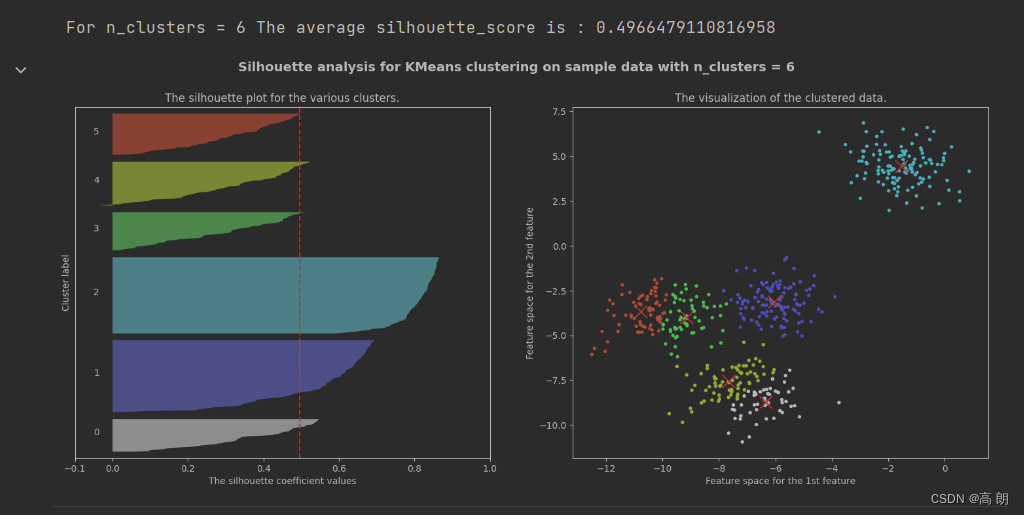

在轮廓系数较高,且每一簇都有贡献的只有n_clusters =2和n_clusters =4,具体选那个根据业务而定。
【图1的纵坐标是样本,每一簇样本的轮廓系数是从小到大排过序的,中间的红色虚线是平均的轮廓系数】
卡林斯基-哈拉巴斯指数
卡林斯基-哈拉巴斯指数(Calinski-Harabaz Index,简称CHI,也被称为方差比标准),Calinski-Harabaz指数越高越好。对于有k个簇的聚类而言,Calinski-Harabaz指数s(k)写作如下公式:
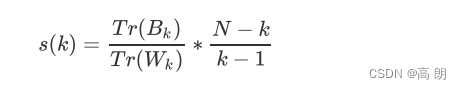
N为数据集中的样本量,k为簇的个数(即类别的个数), B k B_k Bk 是组间离散矩阵,即不同簇之间的协方差矩阵, W k W_k Wk是簇内离散矩阵,即一个簇内数据的协方差矩阵,而 T r Tr Tr表示矩阵的迹。
数据之间的离散程度越高,协方差矩阵的迹就会越大。 簇内离散程度小,簇外离散程度大,对应 T r ( W k ) Tr(W_k) Tr(Wk)小, T r ( B k ) Tr(B _k) Tr(Bk)大,即Calinski-Harabaz指数s(k)越高越好。
from sklearn.metrics import calinski_harabasz_score #Calinski-Harabaz指数
calinski_harabasz_score(X, y_pred)
calinski-Harabaz指数没有界,在凸型的数据上的聚类也会表现虚高。但是比起轮廓系数,它有一个巨大的优点,就是计算非常快速。
init & random_state & n_init:初始质心
如果有足够的时间,K-means一定会收敛,但Inertia可能收敛到局部最小值。
是否能够收敛到真正的最小值很大程度上取决于质心的初始化。
init就是用来帮助我们决定初始化方式的参数。
初始质心放置的位置不同,聚类的结果很可能也会不一样,一个好的质心选择可以让K-Means避免更多的计算,让算法收敛稳定且更快。
一个random_state对应一个质心随机初始化的随机数种子。如果不指定随机数种子,则sklearn中的K-means并不会只选择一个随机模式扔出结果,而会在每个随机数种子下运行多次,并使用结果最好的一个随机数种子来作为初始质心。
我们可以使用参数n_init来选择,每个随机数种子下运行的次数。这个参数不常用到,一般10次,默认是’
auto’,如果我们希望运行的结果更加精确,那我们可以增加这个参数n_init的值来增加每个随机数种子下运行的次数。
init:可输入"k-means++“,“random"或者一个n维数组。这是初始化质心的方法,默认"k-means++”。输入"kmeans++”:一种为K均值聚类选择初始聚类中心的聪明的办法,以加速收敛。如果输入了n维数组,数组的形状应该是(n_clusters,n_features)并给出初始质心。random_state:控制每次质心随机初始化的随机数种子n_init:整数,默认auto,使用不同的质心随机初始化的种子来运行k-means算法的次数。最终结果会是基于Inertia来计算的n_init次连续运行后的最佳输出
n_initwill change from 10 to ‘auto’ in 1.4
初始质心选得好的话,模型会收敛得更快,迭代次数会更少:
max_iter & tol
当质心不再移动,Kmeans算法就会停下来。但在完全收敛之前,我们也可以使用max_iter(最大迭代次数)或者tol(两次迭代间Inertia下降的量),这两个参数来让迭代提前停下来。
当我们的n_clusters选择不符合数据的自然分布,或者我们为了业务需求,必须要填入与数据的自然
分布不合的n_clusters,提前让迭代停下来反而能够提升模型的表现。
max_iter:整数,默认300,单次运行的k-means算法的最大迭代次数tol:浮点数,默认1e-4,两次迭代间Inertia下降的量,如果两次迭代之间Inertia下降的值小于tol所设定的值,迭代就会停下
k_means函数
sklearn.cluster.k_means (X,
n_clusters,
sample_weight=None,
init=’k-means++’,
precompute_distances=’auto’,
n_init=10,
max_iter=300,
verbose=False,
tol=0.0001,
random_state=None,
copy_x=True,
n_jobs=None,
algorithm=’auto’,
return_n_iter=False)
和类得参数基本相同,不过函数调用直接返回结果
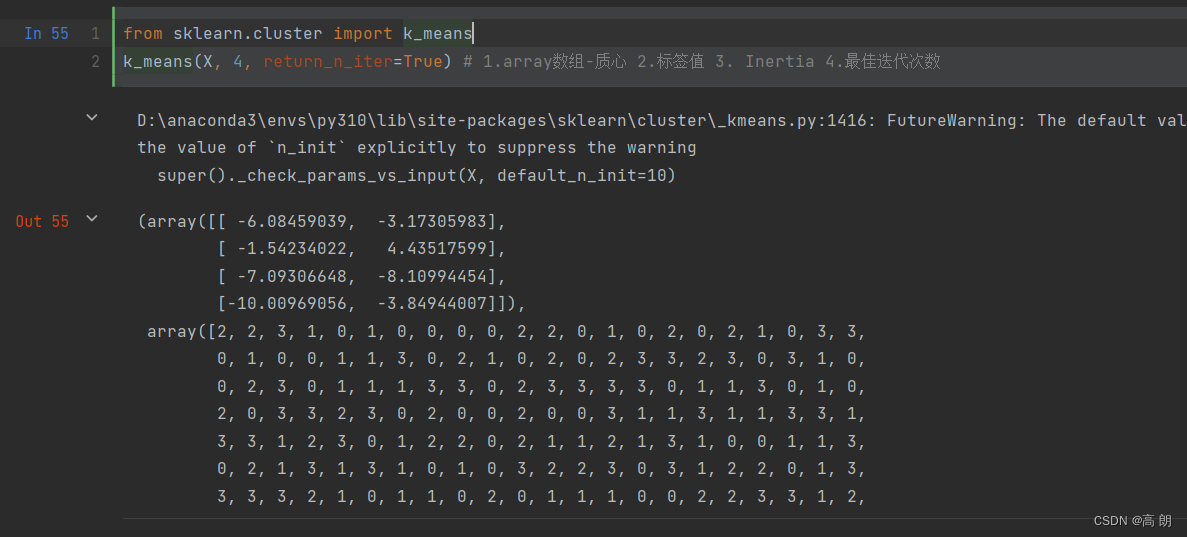
from sklearn.cluster import k_means
k_means(X, 4, return_n_iter=True) # 1.array数组-质心 2.标签值 3. Inertia 4.最佳迭代次数
返回值包括:1.array数组-质心 2.标签值 3. Inertia 4.最佳迭代次数【return_n_iter=True时返回】